10x Genomics ver öffentlichtVisium HDIm Januar 2024-eine räumliche Transkript omik plattform der nächsten Generation, die in der Lage ist, die Gen expression bei nahezu Einzel zell auflösung abzubilden. Konzipiert fürFFPE (Formalin-fixiert, Paraffin-eingebettet)Gewebe, diese Plattform hat erhebliche Aufmerksamkeit von der biomedizin ischen Forschungs gemeinschaft gewonnen.
Bei Omics Empower haben wir Antworten auf die am häufigsten gestellten technischen Fragen zusammen gestellt, die Forscher bei der Planung von Visium HD-Projekten aufgeworfen haben. Dieses Handbuch dient als Einstiegs punkt für das Verständnis der einzigartigen Funktionen, des Workflows, der Beispiel anforderungen und der Daten ausgaben der Plattform.
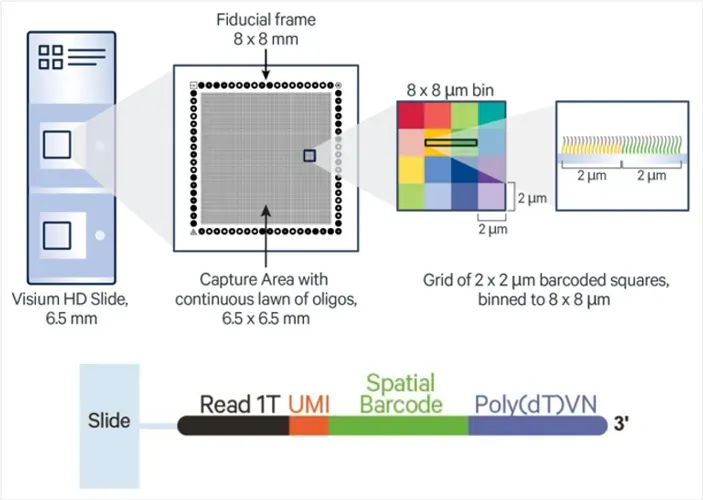
Visium HD stellt eine neu gestaltete Erfassungs folie vor, die eine sub zelluläre Auflösung und eine hohe räumliche Wiedergabe treue bietet:
Jede Folie enthältZwei 6,5 × 6,5mm Erfassungs bereiche.
Die Capture-Bereiche sind dicht gepackt mit2 × 2 µm Barcodierte Oligo-Quadrate.
Vor geschlagene Analyse behälter größe ist8 × 8 µm, ErmöglichenRäumliche Auflösung nahe Einzelzellen.
Jedes Oligo enthält eine Illum ina Read 1T-Sequenz, UMI, einen räumlichen Barcode und einen Poly (dT)-Schwanz zum Einfangen polyadenylierter RNA.
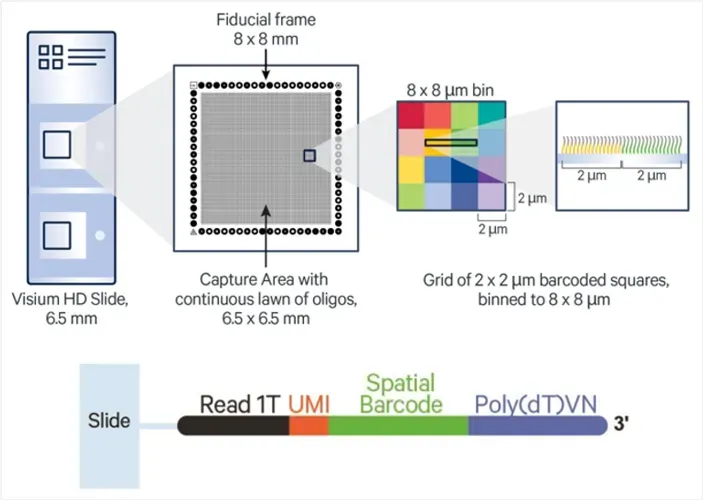
Abbildung 1. Schematische Darstellung des Visium-HD-Dia-Capture-Bereichs (oben) und der Oligo nukleotid struktur (unten)
Visium HD hat dieselben technischen Kern prinzipien wie Visium Cyt Assist (V2), darunter:
(1) Gezielte Sonden basierend auf annot ierten Genen im Genom von Mensch und Maus.
Jede Sonde besteht aus einer linken Seite (LHS) und einer rechten Seite (RHS):LHS enthält einen Teil der Read 2S-Sequenz und eine 25bp-Sequenz, die zur linken Seite der Ziel-mRNA komplementär ist.
RHS enthält eine 25 bp Sequenz, die zur rechten Seite der mRNA komplementär ist, und einen 30 bp Poly (A)-Schwanz.
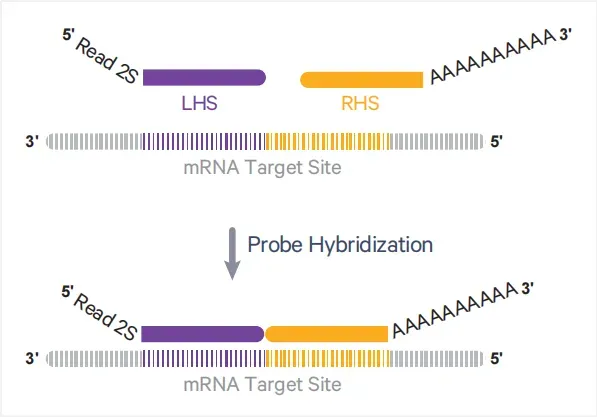
Abbildung 2. Schematische Struktur der Sonde
(2) CytAssist-vermittelte In-situ-Übertragung.
Während des Transfer prozesses ist der Gewebe rutscher mit hybrid isierten Sonden unter Verwendung des CytAssist-Instruments eng mit dem Visium HD-Objektträger ausgerichtet. Die RNase-Behandlung verdaut die Gewebe-RNA und setzt Sonden-mRNA-Hybride frei. Der Poly (A)-Schwanz der Sonde hybrid isiert mit den Poly (dT)-Oligos auf dem Visium-Objektträger und ermöglicht so eine räumliche Erfassung.
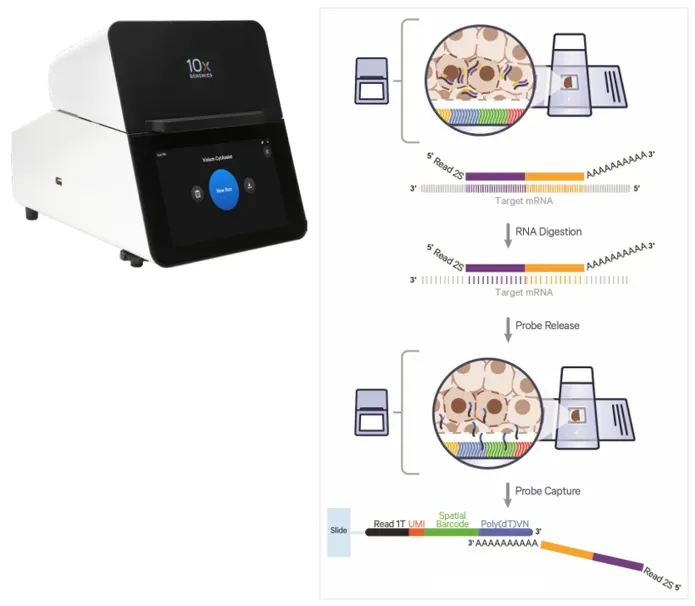
Abbildung 3. Prinzip der Gewebe übertragung über Cyt Assist
Visium HD unterstützt derzeit nur FFPE-Proben aus menschlichen und Maus geweben. Das Proben vorbereitung protokoll ist identisch mit dem von Visium Cyt Assist (V2). Für qualitativ hochwertige Ergebnisse müssen Gewebes chnitte eine gut erhaltene Kern morphologie, eine gute RNA-Integrität und keine Ablösung während der Verarbeitung aufweisen. Zu den wichtigsten Überlegungen gehören:
(1) Paraffin blöcke werden bevorzugt.
(2) Wenn nur FFPE-Objektträger verfügbar sind, stellen Sie sicher, dass die Schnitt dicke bei ordnungs gemäßer Trocknung 5 µm beträgt.
Verwenden Sie 10x empfohlene Folien und befolgen Sie die spezifischen Platzierung richtlinien für jedes Folien modell
Für Gewebe, die zur Ablösung neigen (e.g., B. Haut, Blutgefäße, Fett, Sehne, Brust, Lunge, Dickdarm, mehrkerniges oder Bindegewebe), Adhäsion träger wie Schott H-3D (PN-1800434) werden dringend empfohlen.
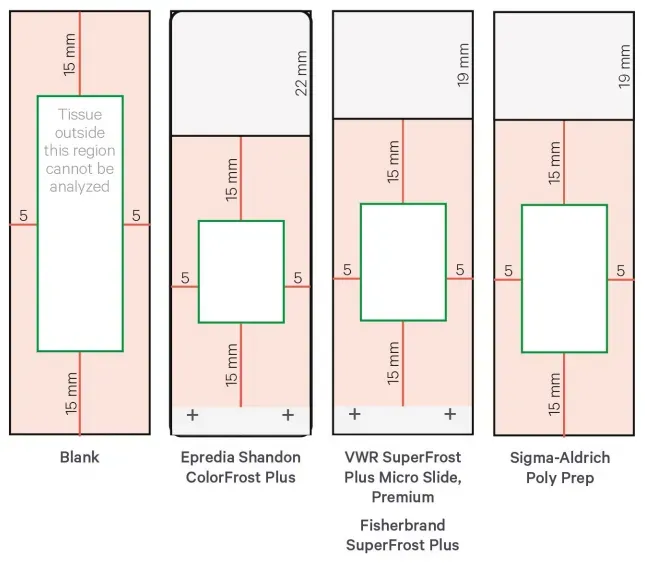
Abbildung 4. Empfohlene Folien typen und Gewebe platzierung bereiche nach 10x Genomik (grün angegeben)
(3) Transport bedingungen: 4 °C. Folien sollten während des gesamten Versands trocken bleiben (siehe Beispiel anleitung für Omics Empower).
(4) RNA-Qualitäts anforderung: DV200 > 30%, mit einem normalen RNA-Profil.
<P>Der Visium HD-Workflow ist identisch mit Visium Cyt Assist (V2) und umfasst die folgenden Schritte:
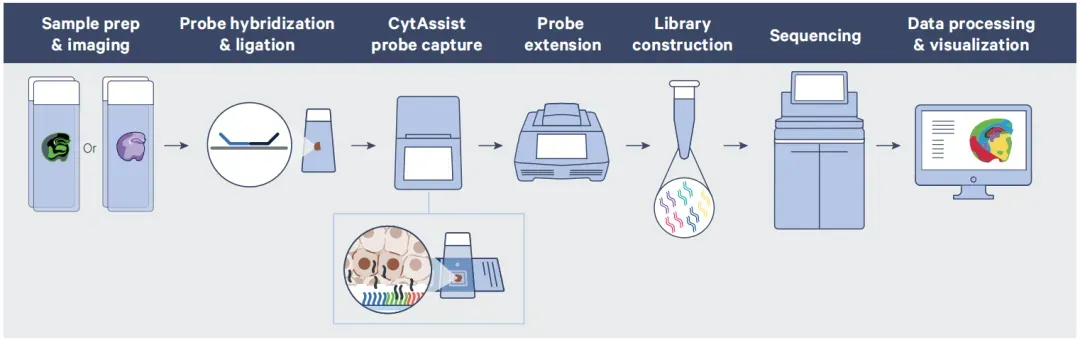
Abbildung 5. Übersicht über den Visium HD-Workflow
(1) Proben vorbereitung und Bildgebung: FFPE-Gewebe wird auf den effektiven Einfang bereich eines 10x empfohlenen Objektträgers geschnitten. Darauf folgen Deparaffinisierung, H & E-Färbung, Bilder scannen, Destin ieren und Decross verknüpfen. Die Sonden hybrid isierung wird unmittelbar danach durchgeführt.
(2) Nach der Hybrid isierung und dem Waschen über Nacht werden die Sonden ligiert.
(3) Das CytAssist-Instrument führt die Folien übertragung durch.
(4) Die Sonden werden auf dem Visium HD-Objektträger mit einem Thermo cycler erweitert.
(5) Erbeutete Sonden werden eluiert und einer Vor verstärkung und Bibliotheks konstruktion unterzogen.
(6) Bibliotheken werden sequenziert und analysiert.
Die Visium HD-Bibliotheks struktur ist wie folgt:
Read 1 enthält den räumlichen Barcode und UMI (Gesamtlänge: 43 bp)
Read 2 enthält die 50 bp Sonden einsatz sequenz
Die Sequenz ierung wird im PE150-Modus durchgeführt, wobei pro Aufnahme bereich ~ 275 Millionen Lese vorgänge empfohlen werden.
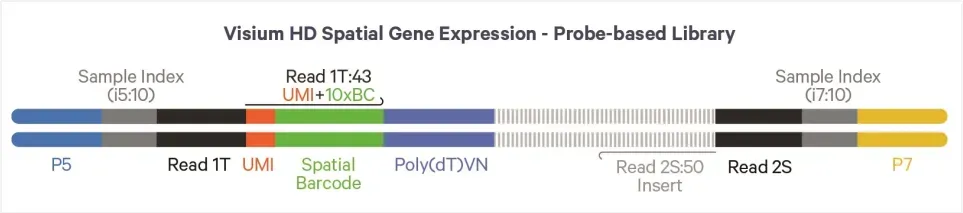
Abbildung 6. Struktur der Visium HD-Sonde-Bibliothek
Da Visium HD für FFPE-Proben verwendet wird, bei denen sich Wasser während des Abschnitts ausbreiten muss, erhöht das Fliesen mehrerer Proben das Risiko einer Ablösung-insbesondere bei zerbrechlichen Geweben. Aus diesem Grund wird von Fliesen grunds ätzlich abgeraten. Bei Bedarf sollten nicht mehr als zwei Gewebes tücke innerhalb desselben Fang bereichs platziert werden.
Für menschliche Proben verwendet Visium HD das gleiche V2-Sonden design wie Visium Cyt Assist (V2) mit drei Sonden paaren pro Gen.
Für Maus-Samples verwendet Visium HD eine verbesserte Version. Während Cyt Assist (V2) nur ein Sonden paar pro Gen (V1) verwendet, verwendet Visium HD drei Sonden paare pro Gen (V2). Dies sorgt für eine verbesserte Detektion effizienz und eine höhere mediane Gen zahl.
10x Genomics hat eine Liste von FFPE-Gewebe typen ver öffentlicht, die für Visium HD validiert sind. Nach unserer Erfahrung schneiden FFPE-Proben, die erfolgreich an Visium Cyt Assist gearbeitet haben, im Allgemeinen auch bei Visium HD gut ab. Umgekehrt ist es unwahr schein lich, dass Samples, die zuvor mit Cyt Assist fehl geschlagen sind, bei Visium HD erfolgreich sind. Für Unterstützung bei bestimmten Muster typen wenden Sie sich bitte an unsereTechnische spezialisten.
Omics Empower ist ein 10x Genomics Certified Service Provider. Wenn Sie daran interessiert sind, wie unsere Dienstleistungen Ihre Forschung unterstützen können, wenden Sie sich bitte an unser Team. Ob Sie Hilfe bei der Proben vorbereitung benötigen,Einzel zell sequenz ierung,Sequenz ierung der räumlichen Transkript omikOder Datenanalyse, können wir jeden Schritt des Prozesses behandeln, um qualitativ hochwertige Ergebnisse zu gewährleisten. Kontaktieren Sie uns heute für eine Beratung!
** Gutschrift: Alle in diesem Artikel dargestellten Zahlen und Daten werden 10x Genomics gut geschrieben, sofern nicht anders angegeben.
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong