
Die Einzel zell-RNA-Sequenz ierung (scRNA-seq) hat das Verständnis des zellulären Verhaltens revolution iert, von Schicksals entscheidungen und Entwicklungs übergängen bis hin zu Reaktionen unter Stress und Krankheit. Ein Schritt bleibt jedoch für fast alle nach gelagerten Analysen von grundlegender Bedeutung-die Identifizierung des Zelltyps.
Wie viele Forscher Ihnen sagen werden, ist eine genaue Anmerkung des Zelltyps wie die Schaffung eines soliden Fundaments für ein Haus: Wenn es instabil ist, wird alles, was oben gebaut wird, unzuverlässig.
In diesem Beitrag führen wir Sie durch gemeinsame Herausforderungen bei der Annotation vom scRNA-seq-Zelltyp-und wie Sie diese mit Zuversicht angehen können.
Nehmen Sie sich einen Moment Zeit, um Ihre Clustering-Parameter-insbesondere die Auflösung-auszuwerten, bevor Sie in eine markierung basierte Annotation einsteigen. Die Auflösung wirkt sich direkt auf die Anzahl und Trennung von Clustern aus, was sich wiederum auf Ihre Fähigkeit auswirkt, aussage kräftige Zelltypen zu unterscheiden.
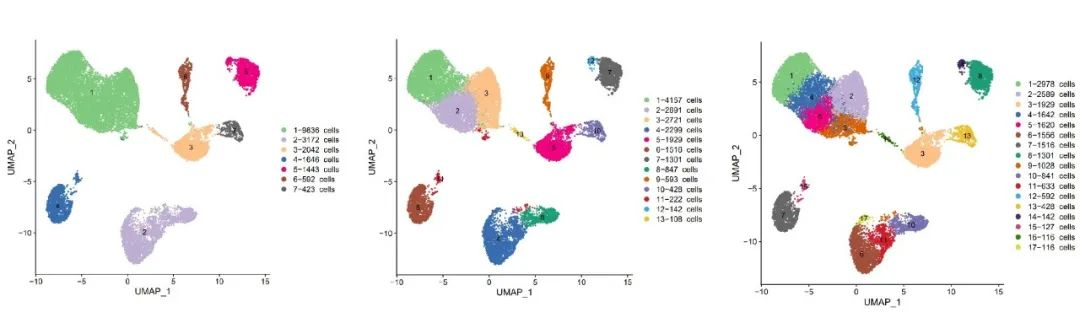
Aber führt eine höhere Auflösung immer zu ident ifizier bareren Zelltypen?
Nicht unbedingt.
Wichtige Überlegungen:
Niedrige AuflösungKann verschiedene Zelltypen zu einem einzigen Cluster zusammenführen und die biologische Hetero genität maskieren.
Hohe AuflösungErhöht die Cluster zahl, enthüllt jedoch nicht unbedingt neue Zelltypen-nur kleinere Teilmengen, was die Annotation erschwert.
Tipps zur Optimierung des Clustering:
1. Untersuchen Sie die Top 10 Marker pro Cluster-sind sie einzigartig und spezifisch?
2. Überprüfen Sie, ob eine hohe Ähnlichkeit zwischen den Clustern vorliegt. Wenn mehrere Cluster gleich aussehen, kann das Zusammenführen gerecht fertigt sein.
3. Wenn ein Cluster Marker aus mehreren Zelltypen anzeigt, versuchen Sie, die Auflösung zu erhöhen.
Sobald das Clustering optimiert ist, ist es an der Zeit, jeden Cluster mit Anmerkungen zu versehen. Es gibt zwei allgemeine Ansätze:
Diese Tools stimmen Ihre Daten mit kuratierten Datensätzen oder Marker-Gen bibliotheken ab:
SingleR: Schnell, einfach zu bedienen (nur Mensch und Maus)
Celaref: Basierend auf der Expressions ähnlichkeit zwischen Datensätzen
Garnett: Maschinelles Lernen basiert, verwendet Marker regeln
Cell Ass sign: Bayes'sches Framework unter Verwendung von Marker-Scores
Diese Werkzeuge eignen sich hervorragend für die vorläufige Annotation, können jedoch in komplexen oder schlecht charakter isierten Geweben nicht genau sein.
Dies ist immer noch der Goldstandard-insbesondere für schlag kräftige Veröffentlichungen.
So kommentieren Sie manuell:
Suchen Sie nach ver öffentlich ter Literatur nach Ihrem Gewebe-, Organismus-und Krankheits modell.
Markern gen listen aus maßgeblichen Quellen zusammenstellen.
Verwenden Sie 2-3 gut etablierte Marker pro Zelltyp.
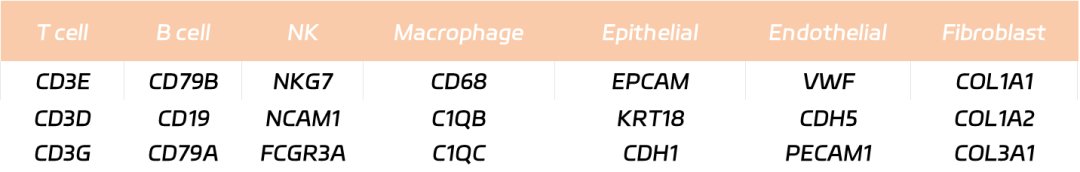
Nützliche Datenbanken:
Erkunden Sie UMAPs, Feature-Plots und Ausdrucks ebenen schnell ohne Codierung. Perfekt für Qualitäts prüfungen und Präsentationen.
Verwenden Sie Seurat oder ähnliche Werkzeuge, um Folgendes zu generieren:
UMAP-Grundstücke
Geigen plots
Punkt grundstücke
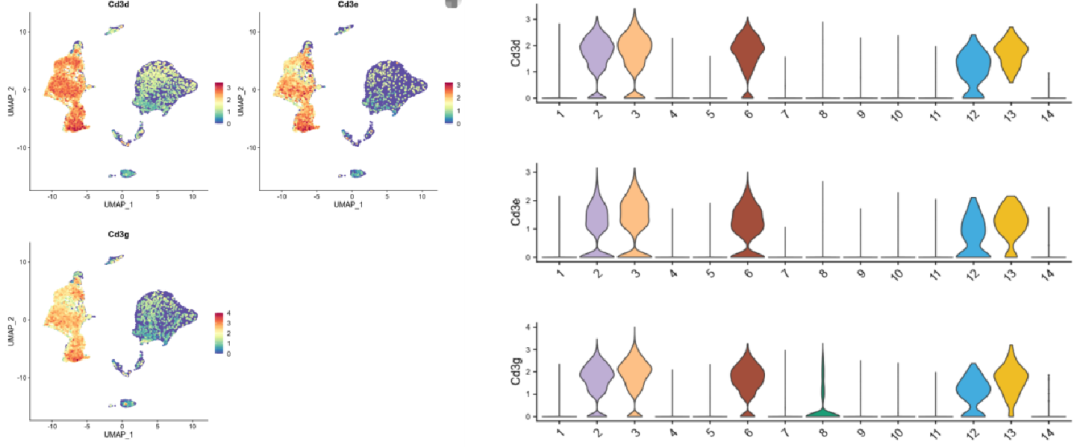
Beispiel: Untersuchen Sie Expres zur Identifizierung von T-ZellenVon CD3D, CD3E und CD3G. Wenn die Cluster 2, 3, 6, 12 und 13 alle diese Marker ausdrücken, können Sie sie getrost als T-Zellen kennzeichnen.
Nicht jeder Cluster passt genau in bekannte Zelltypen. So beheben Sie Fehler:
Zellen von geringer Qualität: Suchen Sie nach ungewöhnlich niedrigen UMI-Zahlen.
Doublets: Co-Expression von zwei nicht verwandten Zelltyp-Markern.
Seltene oder neuartige Populationen: Verwenden Sie Top-Marker und Literatur, um auf Identitäten zu schließen.
Wahrlich unbekannt: Beschriften Sie vorerst als "unbekannt" oder "andere".
BeiOmics Empower, Wir sind spezial isiert auf Ende-zu-EndeEinzelzellen-Sequenz ierungs diensteAuf Ihre Forschungs bedürfnisse zuges chnitten. Mit über 350 Veröffentlichungen und umfassenden Erfahrungen mit Menschen-und Tiermodellen gewähr leistet unser Team eine robuste Anmerkung des Zelltyps, eine aufschluss reiche Downstream-Analyse und fachkundige Unterstützung bei jedem Schritt des Weges.

Benötigen Sie Hilfe beim Annotieren Ihrer Einzelzellen-Daten?
Kontaktieren Sie uns, um mehr über unsere anpassbaren scRNA-seq-Dienste zu erfahren.
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong