
In der einzelligen und räumlichen Transkript omik sind Figuren mehr als nur Illustrationen-sie übersetzen komplexe Datensätze in biologische Bedeutung. Von UMAP-Clustering und Heatmaps bis hin zur Pseudotime-Analyse und Zell-Zell-Kommunikation zeigt jeder Visual isierungstyp verschiedene Aspekte der zellulären Vielfalt und der Gewebe organization.
Dieser Leitfaden hebt gängige Figuren typen in hervorEinzelzelleUndRäumliche Transkript omikForschung und erklärt, wie man sie schnell und genau liest.
Eine technische Workflow-Figur zeigt oft, ob die Studie verwendetEinzelzelleOderRäumliche Transkript omik.
Einzelzelle:Gewebe dissoziation → Einzel zell suspension → Mikro fluidik → Sequenz ierung, häufig mit Droplet-basierten Chip diagrammen.
Räumliche Transkript omik:Tissue-Schnitt → räumliche Hybrid isierung → H & E-Färbung plus Plattform-Chip-Bilder (z. B. 10x Visium).
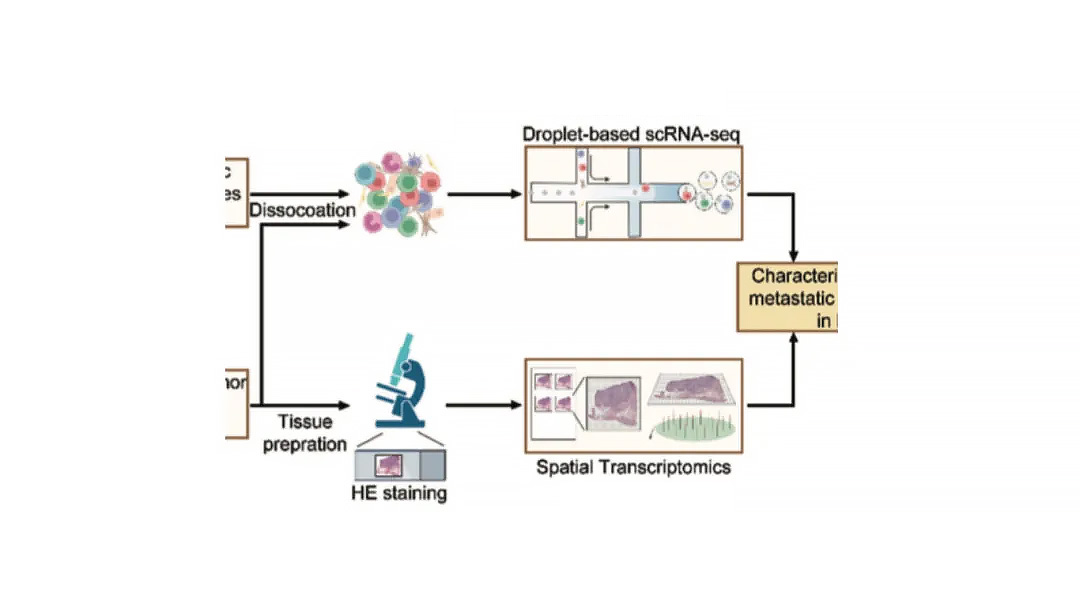
Tipp:Wenn beide Workflows angezeigt werden, integriert die Studie wahr schein lich Einzel zellen-und Geo daten für die kombinierte Analyse.
Diese Zahlen definieren, wie Zellen gruppiert, kommentiert und charakter isiert werden, und bilden die Grundlage für die nach geschaltete Analyse.
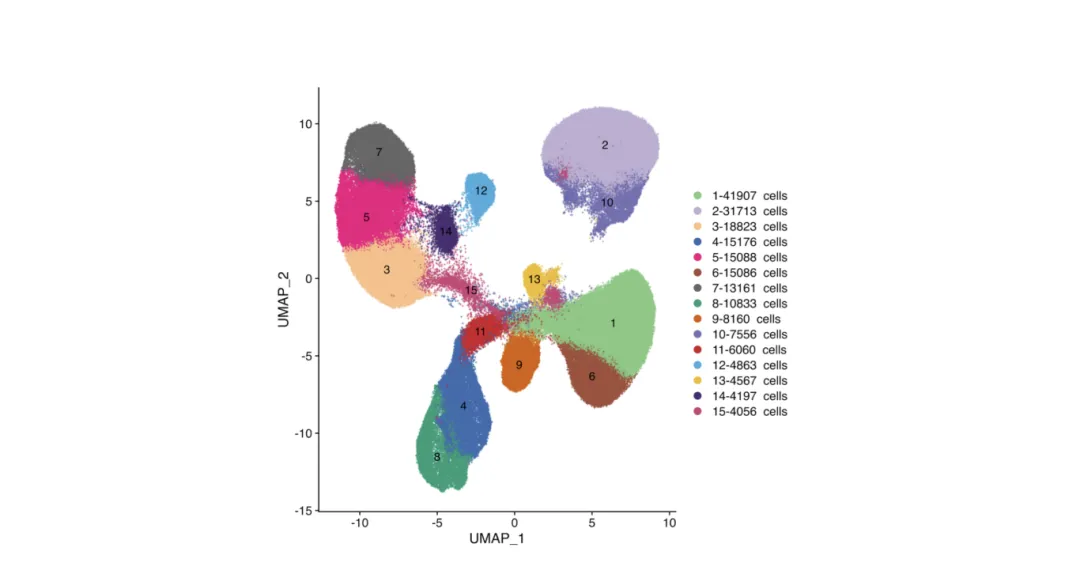
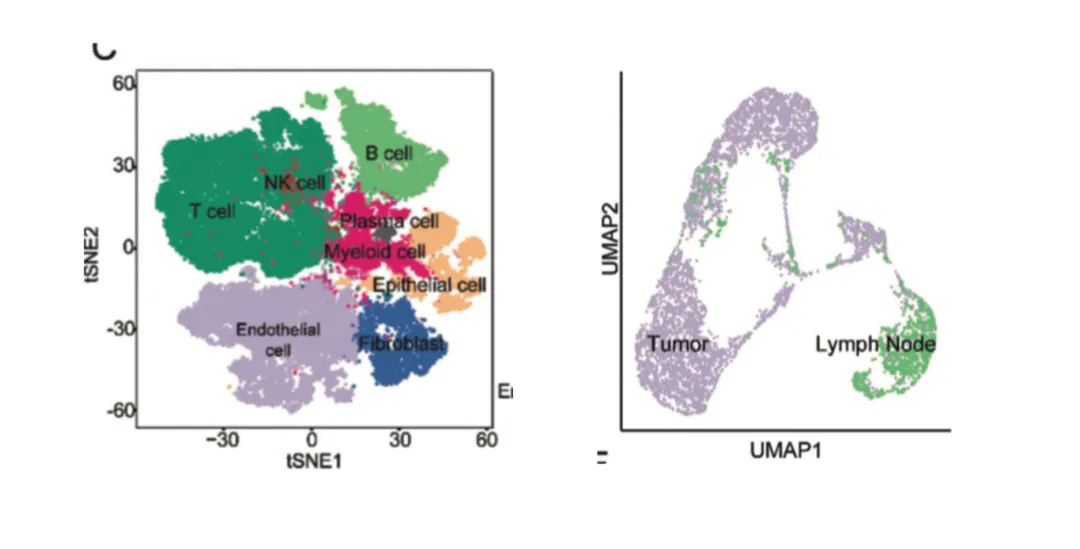
UMAP-und T-SNE-Diagramme sind Standard inEinzelzellen-AnalyseUnd immer häufiger inIntegration der räumlichen Transkript omik.
Zweck:
Reduzieren Sie hoch dimensionale Gen expressions daten in den 2D-oder 3D-Raum, um die Beziehungen von Zelle zu Zelle zu visual isieren.
Wie man liest:
Jeder Punkt= Eine Zelle.
FarbenKann darauf hinweisen:
Cluster-IDs (z. B. Cluster 1, 2, 3…)
Zelltypen (z. B. T-Zellen, B-Zellen, Makrophagen)
Proben gruppen (z. B. Tumor vs. normal)
Gen expressions niveaus für einen ausgewählten Marker.
Fort geschrittene Anwendungen:
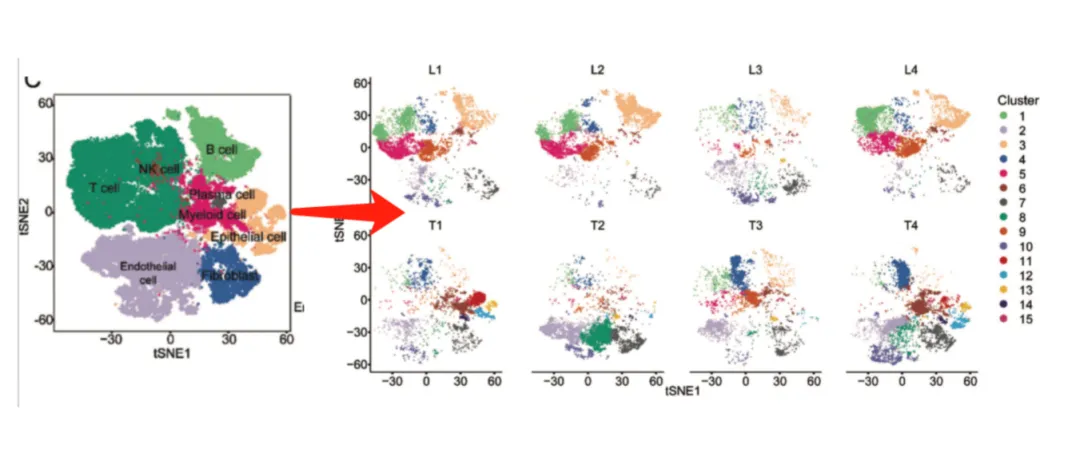
Facettiert durch Stichprobe: Hebt Cluster hervor, die für bestimmte Bedingungen einzigartig sind.
Anmerkung des Zelltyps: Identitäten basierend auf kanonischen Markern zuweisen (z. B. CD3E für T-Zellen, CD19 für B-Zellen). Vermeiden Sie es, „ Cluster = Zelltyp “ohne Marker validierung anzunehmen.
Diese Diagramme dienen als GPS zur Identifizierung funktioneller Zell populationen und zeigen, wo und wie stark Gene exprimiert werden.
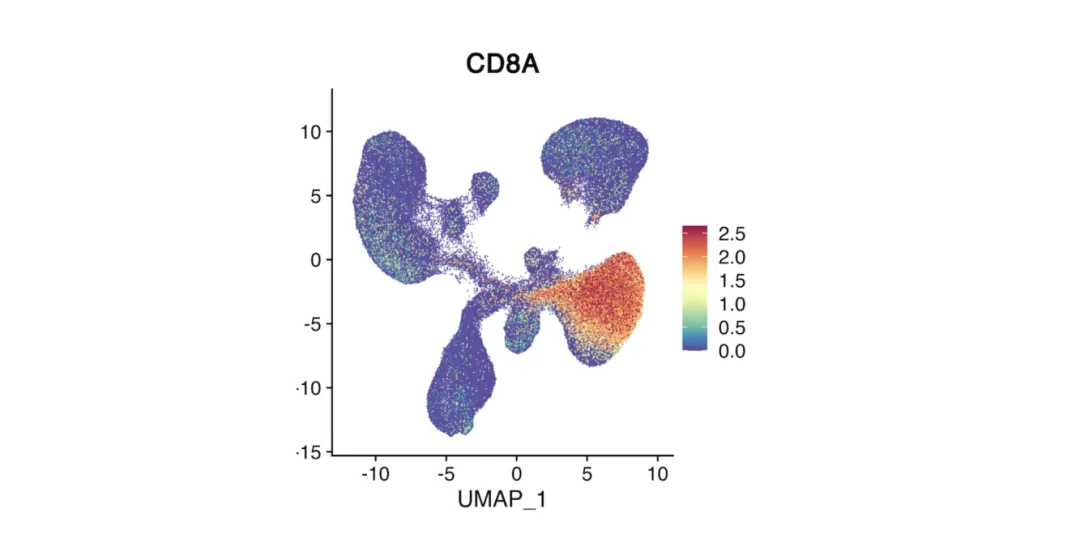
Feature Plot
Überlagert die Expression eines einzelnen Gens auf einemUMAPOderT-SNEHandlung.
Farb intensitätSteht für das Ausdrucks niveau (wärmer = höher).
Bezeichnet den Ort von Zellen, die ein interessiertes Gen exprimieren.
Wird häufig verwendet, um zu überprüfen, ob ein Cluster dem erwarteten Zelltyp entsprichtMarker ausdruck.
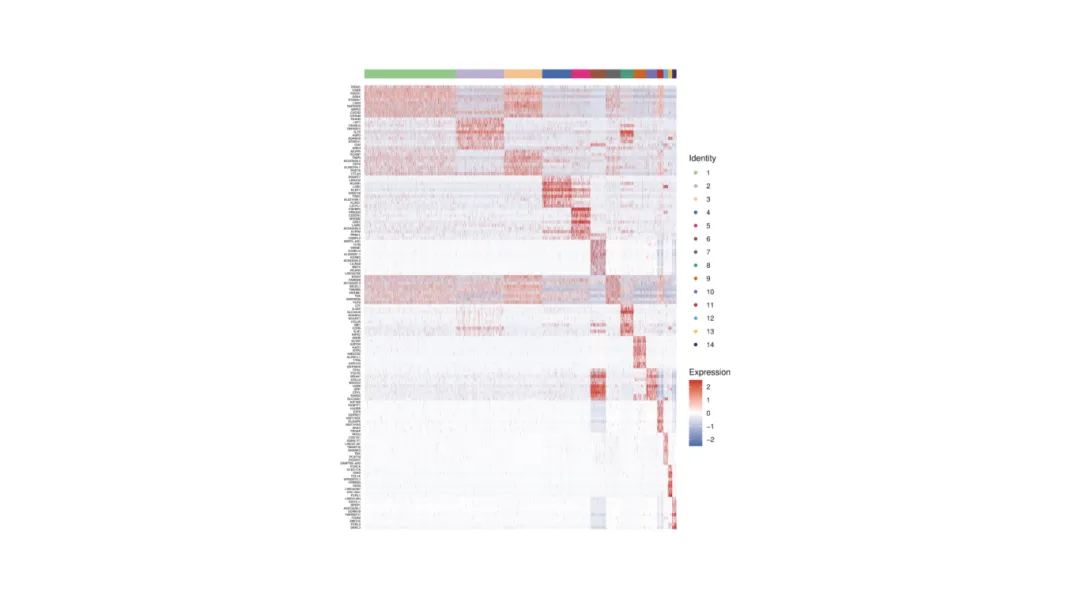
Heatmap
Zeigt Expressions muster mehrerer Gene über Cluster oder Proben hinweg.
Reihen= Cluster oder Proben.
Spalten= Ausgewählte Gene.
FarbverlaufGibt das relative Expressions niveau an.
Oft durch hierarchische Clustering angeordnet, um verwandte Zell gruppen und Signaturen aufzudecken.
Die Heatmap der Top-Marker-Gene über Immun zell cluster hinweg zeigt die linien spezifische Expression.
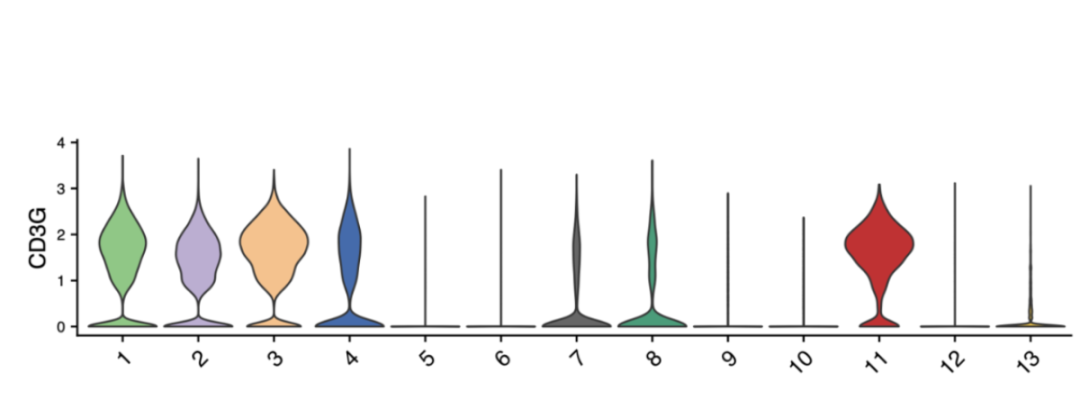
Violine Plot / Box Plot
Zeigt die Verteilung der Expression eines Gens über Cluster an.
Geigen handlung: Breite = Zell dichte; Höhe = Ausdrucks bereich.
Box-Plot: Highlights Median, Quart ile und Ausreißer.
Nützlich zum Vergleich der Variabilität zwischen Zelltypen.
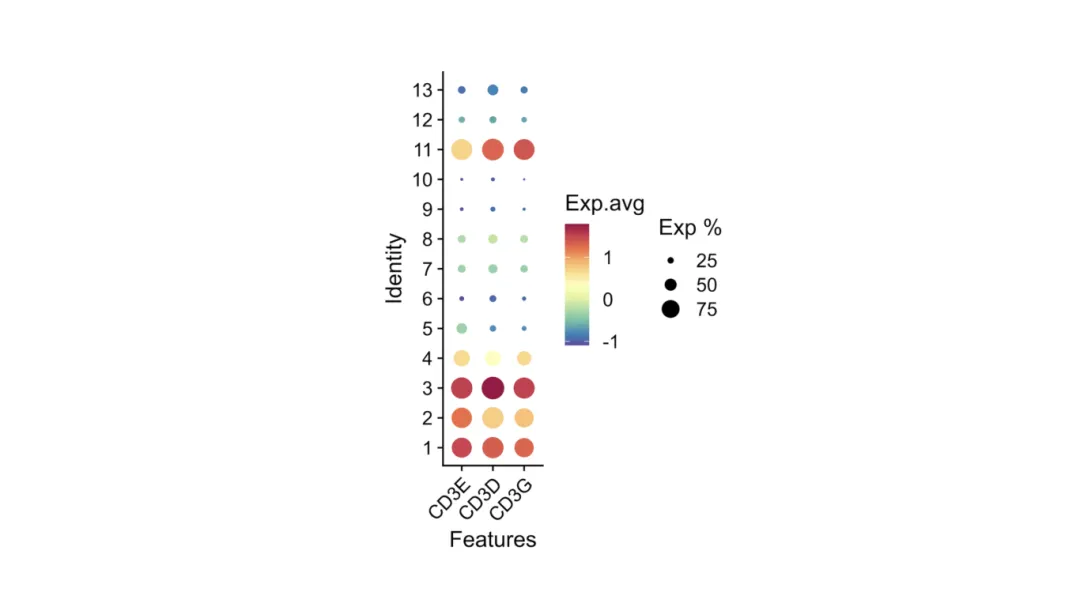
Dot (Bubble) Plot
Fasst die Expression mehrerer Gene über Cluster hinweg zusammen.
Größe= Anteil der Zellen, die das Gen exprimieren.
Farb intensität= Durchschnitt liches Ausdrucks niveau.
Ideal für die Anzeige von Panels von Marker genen in einer Ansicht.
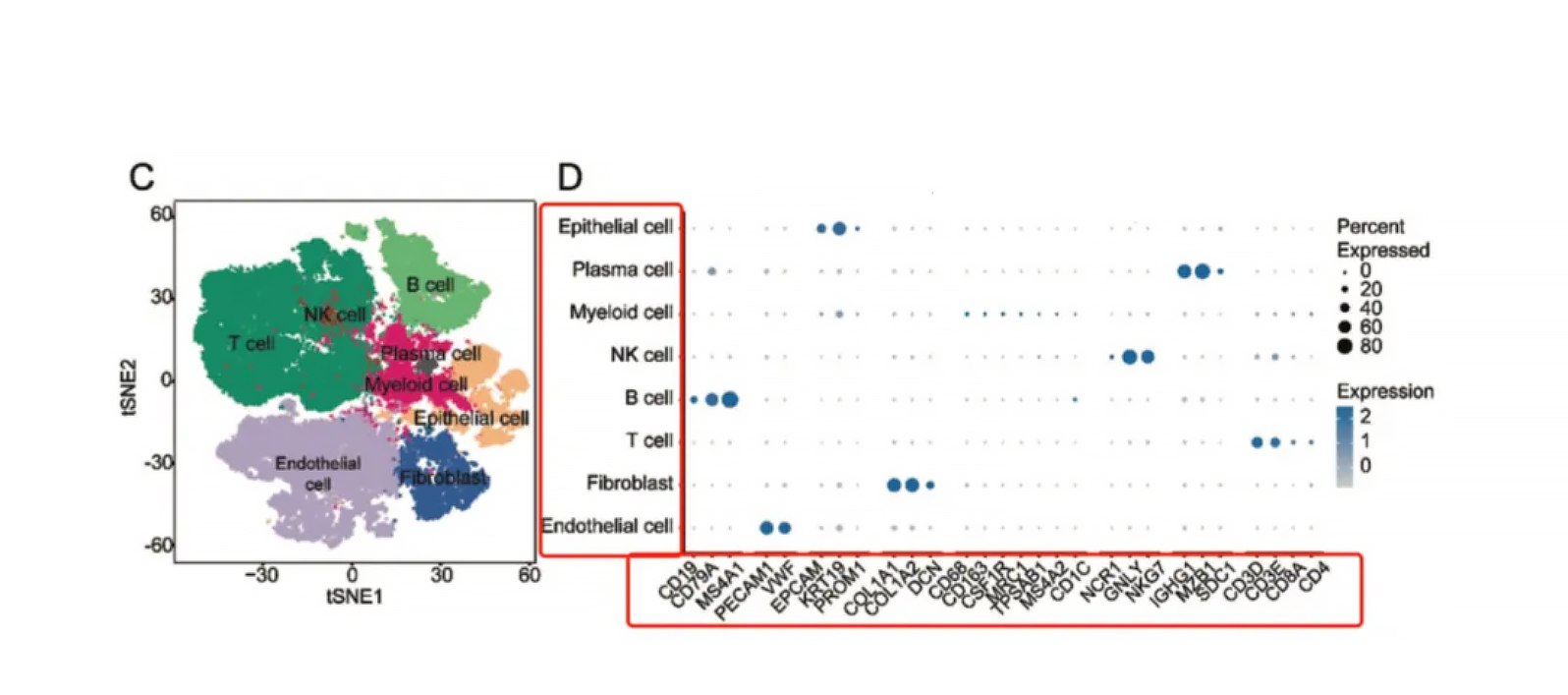
1. Beginnen Sie mit Clustering (UMAP/t-SNE) → validieren Sie mit Heatmaps oder Punkt plots.
2. Verwenden Sie konsistente Farb skalen (rot/hoch, blau/niedrig), um Verwirrung zu vermeiden.
3. Multi-Panel-Layouts, die Clustering und Marker plots Geschwindigkeit interpretation kombinieren.
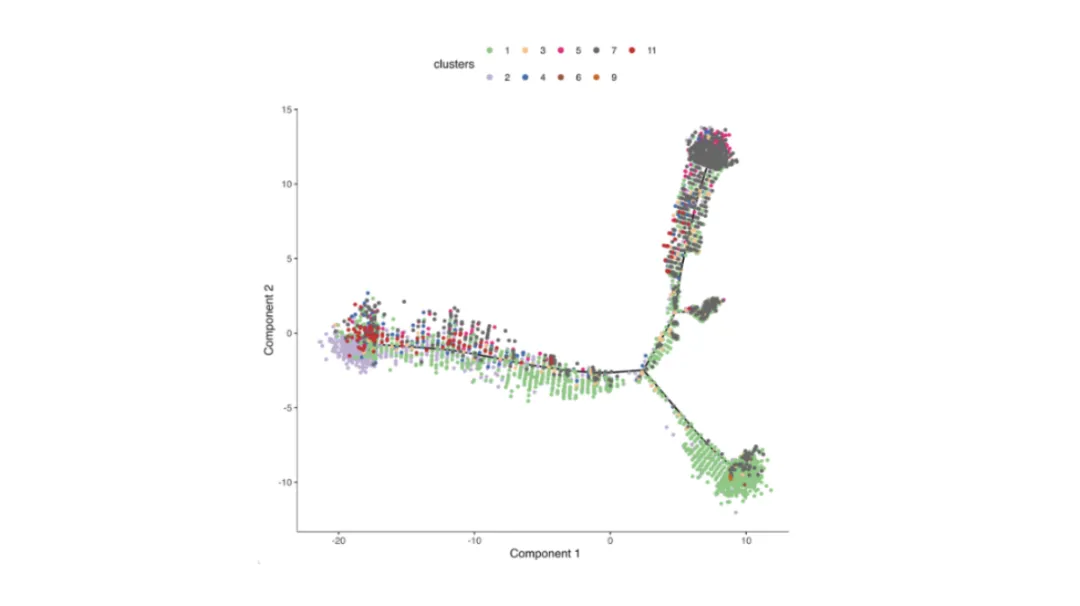
Zweck:Modellieren Sie allmähliche Änderungen der Zell zustände wie Differenzierung oder Aktivierung basierend auf der transkript omis chen Ähnlichkeit.
Wie es generiert wird:Algorithmen wieMonokel,Schleuder, OderScVeloBerechnen Sie die Abstände von Zelle zu Zelle und ordnen Sie sie entlang abgeleiteter Flugbahnen an.
Wie man liest:
Linien= Entwicklungs-oder Aktivierung pfade.
Farben= Pseudotime-Rang, diskrete Stadien oder Expressions gradienten von Schlüssel genen.
Verzweigung spunkte schlagen alternative Differenzierung sergeb nisse vor.
Tipp:Überprüfen Sie die abgeleitete Reihenfolge mit der bekannten Biologie, da die Berechnungs ergebnisse datensatz abhängig sein können.
Vorhersagen Sie funktionelle Wechsel wirkungen zwischen Populationen unter Verwendung bekannter Ligand-Rezeptor-Paare. Zu den Tools gehören CellPhoneDB, CellChat und Niche Net.
Knoten = Zell populationen.
Kanten = vorhergesagte Wechsel wirkungen, gewichtet mitStärke oder Frequenz.
Pathway-Anmerkungen (GO/KEGG) können biologische Themen hervorheben.
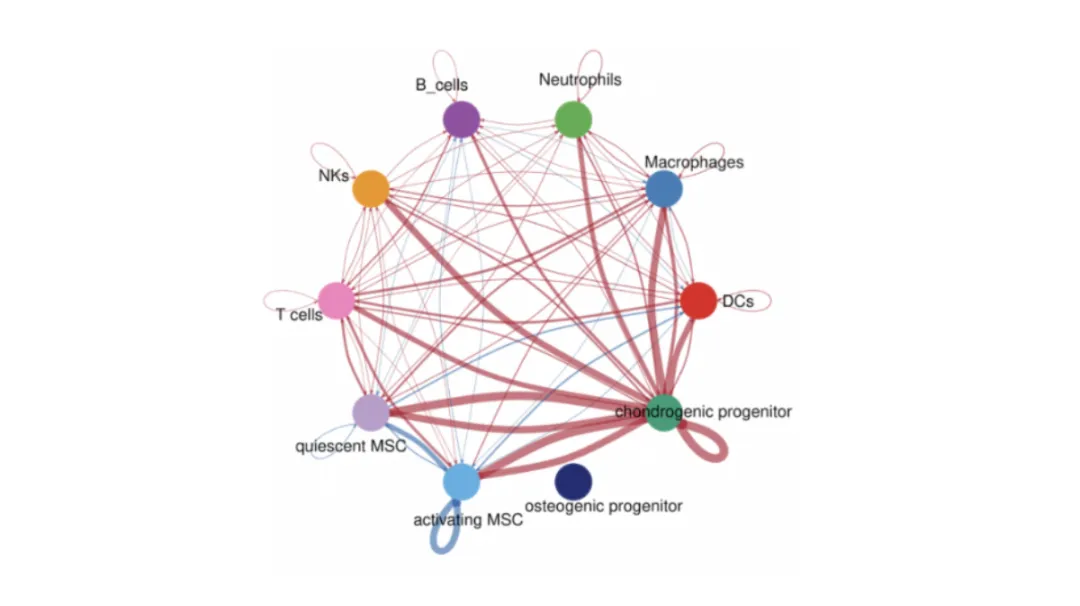
Achsen = Sender-und Empfänger zelltypen.
Größe = Anteil oder Anzahl signifikanter Ligand-Rezeptor-Paare.
Farbe = statistische Signifikanz oder Interaktion stärke.
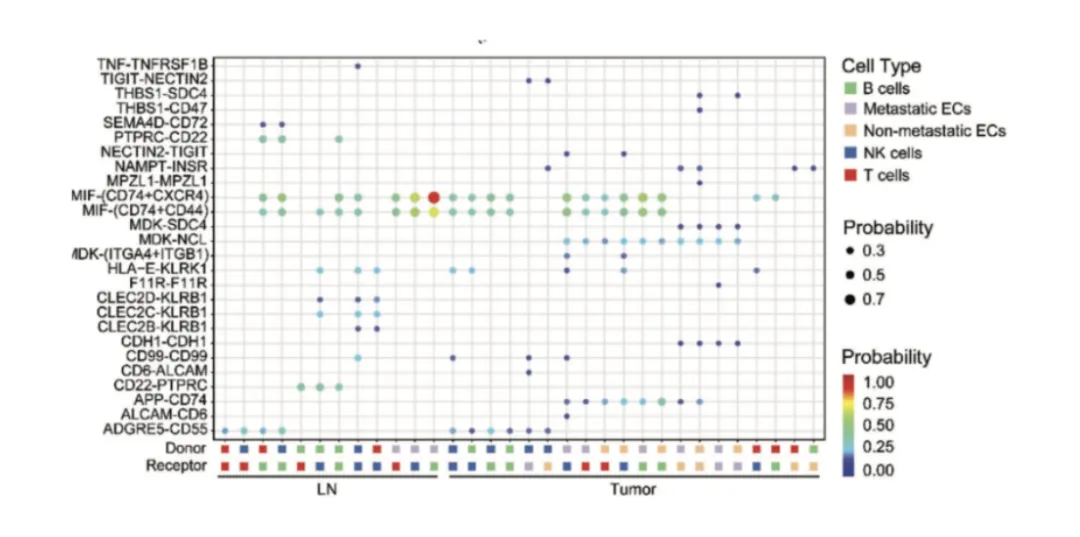
Tipp:Vergleichen Sie mit räumlichen Daten, um fest zustellen, ob vorhergesagte Wechsel wirkungen in benachbarten Zellen auftreten.
Zahlen inEinzelzellen-und räumliche Transkript omikArbeiten Sie am besten, wenn Sie sequenziert werden, um die Leser von der breiten Bevölkerungs struktur zu feinkörnigen biologischen Mechanismen zu führen.
Beispiel-Workflow:
1. Populationen identifizieren-UMAP/t-SNE-Clustering.
2. Markierungen validieren-Feature plots, Heatmaps oder Dot Plots.
3. Erkunden Sie die Dynamik-Pseudo time Trajektorien.
4. Interaktionen verstehen-Netzwerk-oder Blasen plots.
5. Bestätigen Sie im Weltraum-räumliche Transkript omik karten.
Dieser Fortschritt verbindetZell identität→Funktions zustand→Räumliche OrganisationUnd schafft eine klare und logische Erzählung.
InEinzellige und räumliche Transkript omikZahlen sind mehr als nur visuelle Zusammenfassungen-sie sind Analyse werkzeuge, die Sequenz ierungs daten mit biologischen Erkenntnissen verbinden. Wenn Sie wissen, wie UMAPs, Feature-Plots, Heatmaps, Pseudotime-Trajektorien und Kommunikation netzwerke gelesen werden, können Forscher Studien schneller interpretieren und ihre eigene Arbeit klar präsentieren.
Die Beherrschung dieser Visual isierung stech niken ist unerlässlich, um komplexe Einzel zellen-und Geo daten zu verstehen. BeiOmics EmpowerWir verwenden dieselben Ansätze in unseren Service projekten-Rohdaten in klare, publikation fähige Erkenntnisse für Forscher weltweit zu verwandeln.
Unsere Labor plattformen umfassen10x GenomikChrom,Visium, UndXeniumFür Einzel zellen-und räumliche Transkript omik mit hohem Durchsatz, BGI Stereo-Seq für räumliche Kartierung mit ultra hoher Auflösung undMobiDropFür flexible mikro fluid ische Einzel zell analyze.
Wenn Sie brauchenEinzelzelleUndRäumliche Transkript omikAnalyse wie die Beispiele in diesem Blog, kann unser Team helfen, den Workflow zu entwerfen, qualitativ hochwertige Daten zu generieren und umsetzbare Ergebnisse zu liefern.
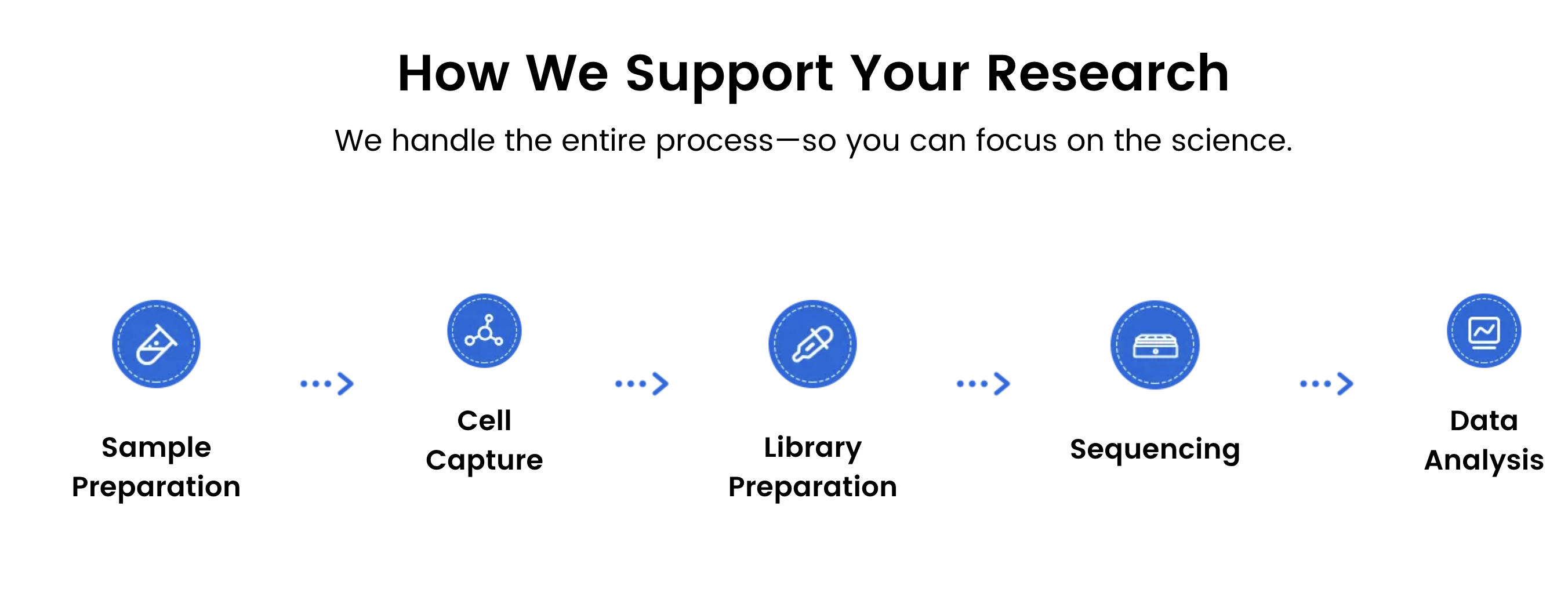
Seit 2018bietet Omics Empower spezial isierte Forschungs dienstleistungen in der Einzel zell-und räumlichen Transkript omik an.
Wir unterstützen akademische Labore, Biotech-Unternehmen und Forschungs kranken häuser bei der zuverlässigen Projekt durchführung in vollem Umfang-von der Proben vorbereitung bis zur Bioinformatik-Analyse.
Mit Labors in Asien, Europa und Nordamerika bieten wir lokalisierte Projekt abwicklung, schnellere Bearbeitungs zeiten und reaktions schnelle Kommunikation in jeder Phase.
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong