Das Verständnis, wie sich Zellen in ihrer nativen Gewebe umgebung verhalten, ist sowohl für die biologische Grundlagen forschung als auch für translation ale Studien von entscheidender Bedeutung. Jede Zelle enthält nicht nur molekulare Informationen, sondern auch einen räumlichen Kontext, der Einblicke in Entwicklung, Krankheits progression und Gewebes truktur geben kann.
Um dieses Maß an Einsicht zu unterstützen,10x GenomikHat sich entwickeltXenium in Situ, Eine räumliche Transkript omik plattform der nächsten Generation, die eine einzellige und sogar sub zelluläre Auflösung bietet. Im Gegensatz zu herkömmlichen Technologien, die auf der In-situ-Erfassung gefolgt von Sequenz ierung beruhen, verwendet XeniumRollkreis-Verstärkung auf Vorhänge schloss sonden basis (RCA)UndFluoreszenz bildgebung zur Ermöglich ung einer hoch empfindlichen, spezifischen und multiplex ierten Gen expressions detektion-Alles innerhalb intakter Gewebes chnitte.
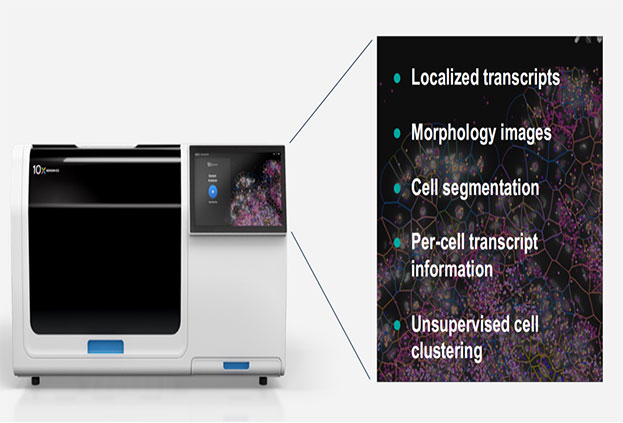
Abbildung 1. Überblick über die Xenium-In-Situ-Technologie
Xenium verwendet Vorhänge schloss sonden, die zwei gen spezifische Bindungs arme und eine zentrale Region aufweisen, die mit fluor zieren den Auslese sonden hybrid isiert werden kann. Sobald beide Enden genau mit der Ziel-mRNA in situ hybrid isieren, bildet die Sonde eine kreisförmige Struktur, die sich unter ziehtRollende Kreis verstärkung. Dieser Prozess erzeugt lokalisierte DNA-Conca temer, die reich an Auslese sequenzen sind.
Diese amplifi zierten Produkte werden sequentiell mit fluor zieren den Sonden hybrid isiert und abgebildet, was zu räumlich codierten Fluoreszenz barcodes führt, die das interessierende Gen identifizieren. Die Sonden konzentrationen können auf der Grundlage der erwarteten Expressions niveaus fein angepasst werden, wodurch beide optimiert werdenEmpfindlichkeit und SpezifitätFür jedes Zielgen.
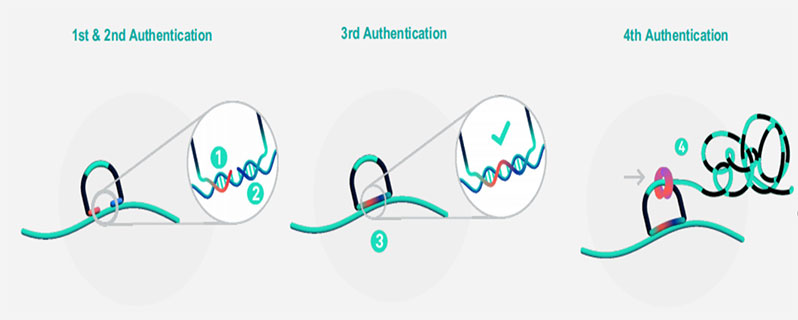
Abbildung 2. Workflow der Vorhänge schloss sonden Hybrid isierung und Rolling Circle Amplifi kation
Gewebe abschnitte (frisch gefroren oder FFPE) werden auf Xenium rutschen platziert. Frisch gefrorene Proben werden fixiert und permeabilisiert; FFPE-Proben werden ent wachst und durchlaufen eine Umkehrung der Vernetzung.
Vorhänge schloss sonden hybrid isieren, um mRNA zu zielen und bei korrekter Bindung kreisförmige Strukturen zu bilden. RCA erzeugt gen spezifische Amplika direkt im Gewebe.
Die Probe wird zur Zell segment ierung gefärbt (z. B. Membran-und Kern farbstoffe), die Auto fluoreszenz wird abgeschreckt und DAPI wird zur Kern markierung verwendet.
Fluor zierende Sonden hybrid isieren mit den RCA-Produkten, und die hoch auflösende Bildgebung erfasst die räumlichen Barcodes. Die resultierenden Bilder werden dekodiert, um die Gen identität und den räumlichen Ort zu bestimmen.
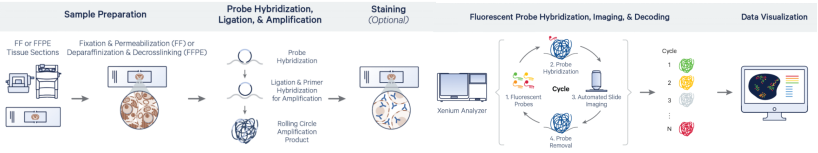
Abbildung 3. Übersicht über den Xenium-Workflow
Im Gegensatz zur Visium HD-Plattform, die nach der Sonden erfassung räumliche Barco dierung und Sequenz ierung verwendet,Xenium ident ifi ziert Transkripte über Fluoreszenz-basierte In-situ-Hybrid isierung. Jedes Gen wird durch einen eindeutigen fluor zieren den Barcode nachgewiesen, der eine direkte Lokal isierung an der Einzelzelle ermöglicht-oder sogarSub zelluläre Ebene.
Zusätzlich erfasst Xenium aViel größere Gewebe flächePro Folie, was eine breitere räumliche Abdeckung ermöglicht, ohne die Auflösung zu beeinträchtigen.
Abbildung 4. Vergleich zwischen Xenium und Visium HD-Folien
Xenium erreichtHohe Reproduzier barkeit über Gewebe typen hinweg. Beispiels weise zeigen benachbarte Abschnitte, die mit dem Xenium 5000-Panel getestet wurden, Transkript korrelation koeffizienten von bis zu0,98.
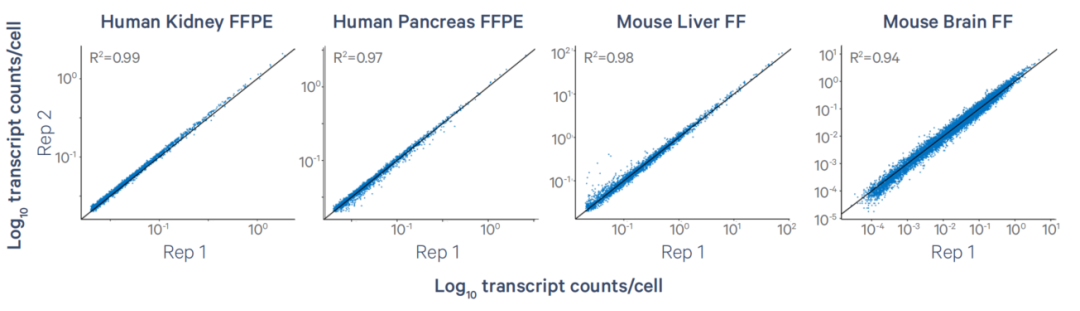
Abbildung 5. Xenium 5000 Panel Leistung über Arten hinweg
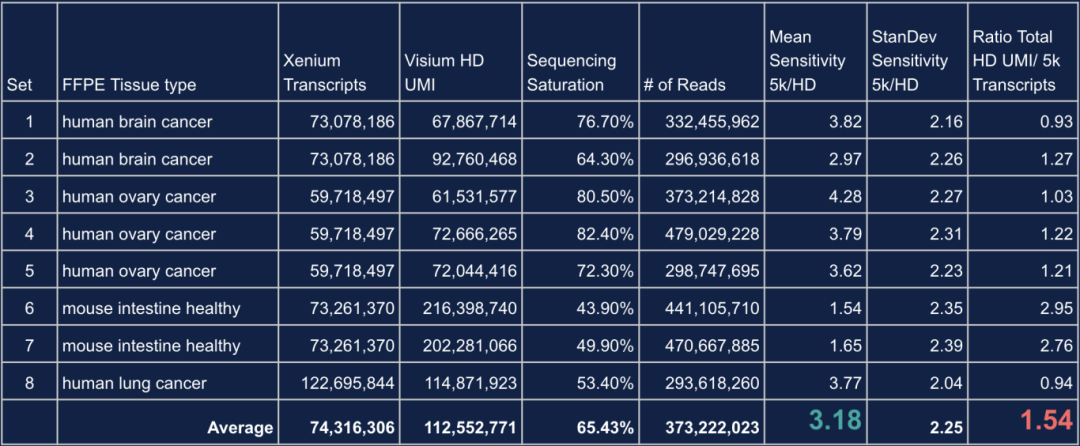
Die Vorhänge schloss sonde und RCA-basierte Erkennungs methode bietetHohe Empfindlichkeit, Einschl ießlich Nachweis vonIso formen und SNPs. Im Vergleich zu Visium HD demonstriert Xenium:
3,18 × höheres Einzel gen Empfindlichkeit, Abhängig von der Sequenz ierungs tiefe
Etwas geringere Gesamt transkript ausbeute (~ 1,54 × weniger als bei Visium HD), was die komplementären Stärken zwischen den Plattformen hervorhebt
Tabelle 1. Vergleich der Leistungs metriken zwischen Visium HD und Xenium
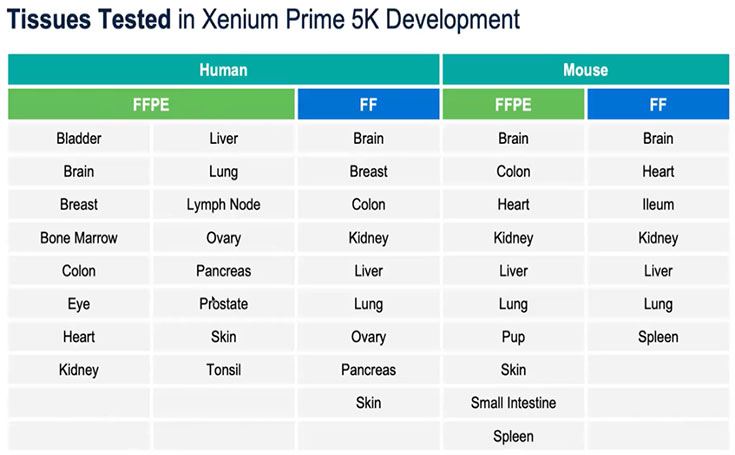
Xenium bietet mehrere Panel-Optionen, um verschiedene Forschungs anforderungen zu erfüllen:
AVorgefertigtes 5000-Gen-PanelFür ein breites Screening
Die Fähigkeit zuBis zu 100 zusätzliche Gene anpassenOben auf dem Kern panel
Vollständig benutzer definierte Paneele bis zu480 Gene, Verfügbar für fast jede Art
Diese Flexibilität unterstützt sowohl entdeckungs basierte als auch hypothesen getriebene Forschung.
Tabelle 2. Xenium 5000 Panel Kompatibilität mit menschlichen und Maus-Gewebe
Eine genaue Zell segment ierung ist entscheidend für die Definition von Zelltypen und die räumliche Organisation. Xenium stellt vorMultimodale Segment ierungKombination mehrerer fluor zieren der Flecken und maschinelles Lernen, um Zellgrenzen objektiv zu definieren-selbst für unregelmäßig geformte Zellen wie Fibroblasten.
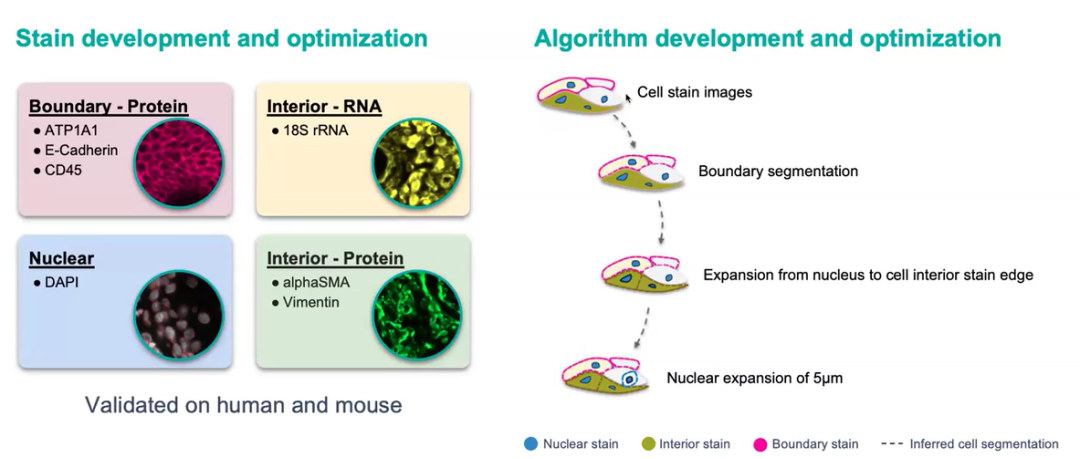
Abbildung 6. Multimodaler Segment ierungs workflow
Dies überwindet die Einschränkungen der traditionellen nukleus basierten Segment ierung, die die Morphologie der sphärischen Zellen voraus setzt.
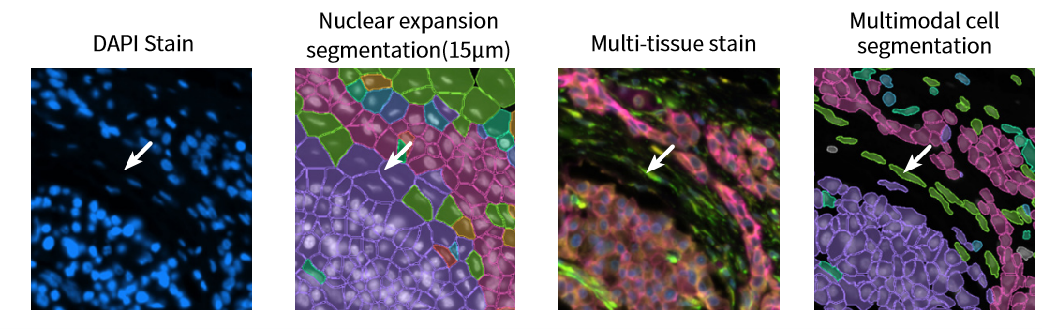
Abbildung 7. Verbesserte Genauigkeit bei UnregelmäßigkeitenZell morphologien
Der zerstörung freie Assay von Xenium bewahrt die Gewebe morphologie und ermöglicht es Forschern, Follow-up-Assays (z. B. Immun fluoreszenz oder Histologie) im selben FF-oder FFPE-Abschnitt durch zuführen. Dies öffnet die Tür zu einer echten Multi-Omic-Analyse von einem einzigen Objektträger aus.
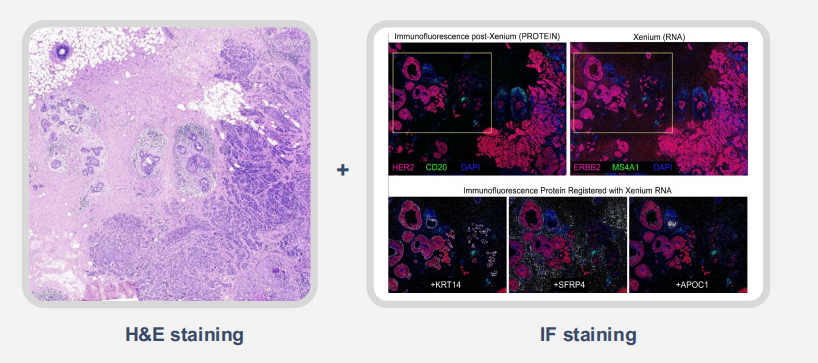
Abbildung 8. Post-Xenium-Kompatibilität mit zusätzlichen Assays
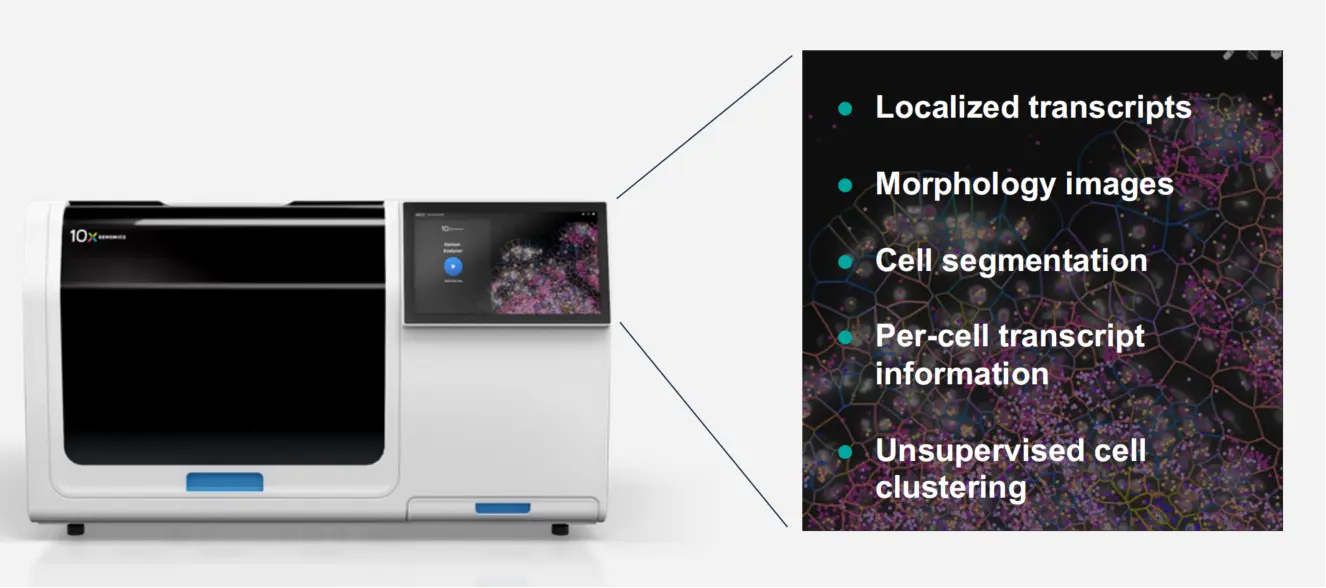
Xenium umfasst leistungs starke Onboard-Software (Xenium-Onboard-Analyse, XOA), Die Daten während der Bildgebung in Echtzeit verarbeitet und decodiert.
Für die nach gelagerte Analyse,Xenium ExplorerBietet intuitive Visual isierung von:
Gewebe morphologie
Zell segment ierung und Klassifizierung
Transkript dichte und räumliche Verteilung
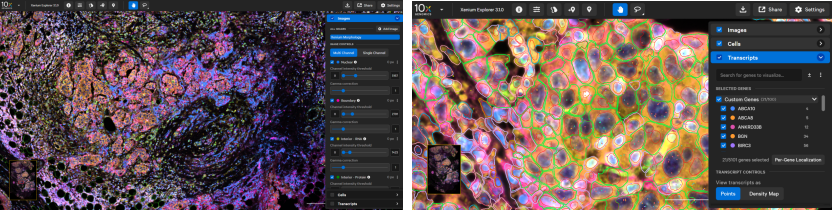
Abbildung 9. Xenium Explorer Ausgabe der FFPE-Brustkrebs probe
Im Vergleich zu herkömmlichen In-situ-Hybrid isierungs techniken bietet Xenium eine schnelle räumliche Profilierung von Kandidaten genen mit hohem Durchsatz sowohl auf Einzel zell-als auch auf sub zellulärer Ebene. Sein fortschritt licher multimodaler Zell segment ierungs algorithmus ermöglicht eine genauere Abgrenzung von Zellen mit unregelmäßigen Formen oder unterschied lichen Größen, eine häufige Herausforderung in komplexen Gewebe umgebungen.
In solchen Szenarien,Xenium übertrifft frühere Plattformen wie Visium V1, V2 und HDDamit eignet es sich besonders für Studien, die eine hohe Auflösung und räumliche Präzision erfordern.
Xenium lässt sich auch nahtlos in Einzelzellen-RNA-seq und andere räumliche Transkript omik plattformen integrieren. Ein gemeinsamer Workflow besteht darin, potenzielle Biomarker zu identifizieren, gefolgt von einer gezielten, räumlich aufgelösten Validierung mithilfe von Xenium-Panels. Dieser zweistufige Ansatz ist zu einer Standards trategie für die räumliche transkript omische Validierung und die Entdeckung von Biomarkern geworden.
BeiOmics Empower, Wir sind spezial isiert auf die IntegrationXeniumMitEinzelzellen-RNA-Sequenz ierungUnd andere räumliche Transkript omik plattformen. Mit umfassender Projekte rfahrung unterstützen wir Forscher über den gesamten Workflow hinweg-von der Proben vorbereitung bis zur Bioinformatik-Analyse.
Wenn Sie ein räumliches Biologie projekt planen, fühlen Sie sich freiPlanen Sie ein Treffen mit unserem wissenschaft lichen Team. Wir sind hier, um Ihnen zu helfen, das Beste aus Xenium heraus zu holen und effiziente, wirkungsvolle Experimente zu entwerfen.
* Gutschrift: Alle in diesem Artikel dargestellten Zahlen und Daten werden 10x Genomics gut geschrieben, sofern nicht anders angegeben.
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong