Ja-die ver öffentlichte Methode und das öffentliche Browser zielPflanzenUnd Referenz pflanzen atlanten.

Wenn Sie Schwierigkeiten haben, Pflanzen zelltypen zu kennzeichnen, da klassische Marker nicht über Arten oder Gewebe hinweg übersetzt werden, bietet der OMG-Browser einen Workflow ohne Code, der auf Ortho logen Marker Groups (OMGs) basiert. Es ordnet Ihre Cluster marker Ortho gruppen zu, testet die Signifikanz und hebt wahr schein liche Übereinstimmungen mit dem Zelltyp hervor, sodass Sie schneller vom Clustering zur biologischen Interpretation wechseln können. Der Ansatz wurde ver öffentlicht inKommunikation Natur(2. Januar 2025).
Im Gegensatz zu Tiermodellen können Marker vom Typ Pflanzen zell spärlich oder spezies spezifisch sein. Arten übergreifende Integration ist auch nicht trivial und rechnerisch schwer. Die OMG-Framework-Seite-unternimmt dies durch einen VergleichGemeinsame ortho loge Marker gruppenZwischen Ihrem Datensatz und einem Referenz atlas und verwenden Sie dann den genauen Test von Fisher, um die Signifikanz der Überlappung zu quantifizieren.
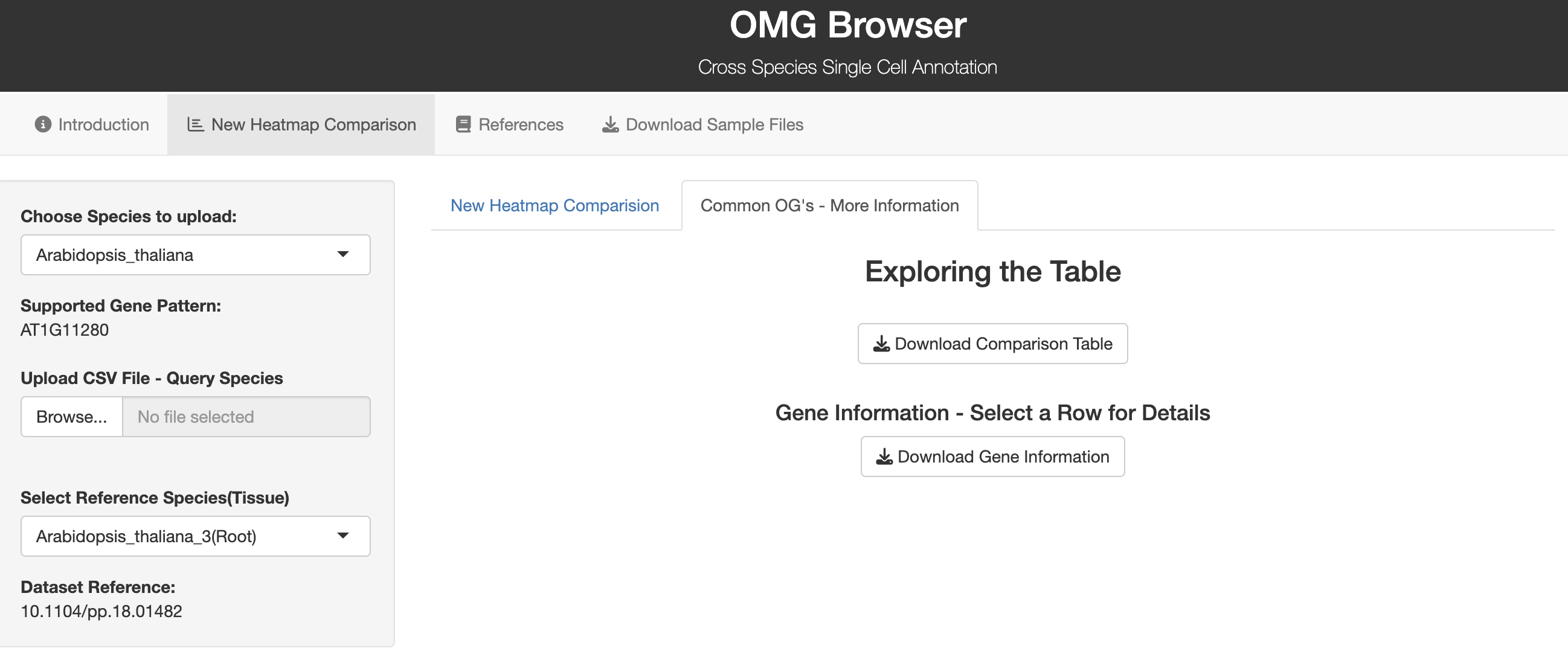
Der OMG-Browser ist ein Web-Tool, das den OMG-Workflow auf benutzer freundliche Weise implementiert-keine Codierung erforderlich. Sie laden Cluster-Marker-Gene hoch, wählen Spezies und Gewebe aus und erhalten eine Heatmap mit-log10(p-Wert) für jeden Cluster-zu-Zelle-Typ-Vergleich. Wichtige Übereinstimmungen werden verpackt, damit Sie schnell auf wahr schein liche Identitäten schließen können. Die zugrunde liegende Methode nutzt Ortho Finder zum Erstellen von Ortho gruppen und führt dann Statistiken zu gemeinsam genutzten Markern durch.
1.Wählen Sie Ihre Zielart.Der Browser zeigt akzeptierte Gen symbol formate für diese Art.
2.Laden Sie Ihre Marker liste (CSV) hoch.Stellen Sie sicher, dass die Symbole mit dem gewünschten Format übereinstimmen (siehe Beispiel datei des Werkzeugs).
3.Wählen Sie eine Referenz art/Gewebe.Das Tool berechnet Überschneidungen und rendert eine Heatmap. Laden Sie die Ergebnis tabelle für die Downstream-Qualitäts kontrolle herunter.
Wo man es versucht:OMG Browser (orthomarkergenes.org).Das öffentliche GitHub-Repo dokumentiert die Methode und Links zum Live-Browser.
In den öffentlichen Materialien und im Repo werden mehrere Pflanzenarten aufgeführt, die üblicher weise im Workflow verwendet werden (z.Arabi dopsis, Tomate, Reis, Mais, Pappel, Tabak, Baumwolle, ImmergrünUsw.) mit einem breiteren Atlas mit 15 Arten, der beim Benchmarking verwendet wird. Überprüfen Sie vor der Analyse immer den neuesten Browser-Build auf Abdeckung.
Clustering-Granularität.Extrem feines Clustering kann kleine Cluster mit zu wenigen zuverlässigen Markern erzeugen, wodurch das Annotation vertrauen verringert wird. Beginnen Sie mit einer biologisch vernünftigen Auflösung und verfeinern Sie sie dann. (In der Methode besprochen.)
Marker auswahl.Verwenden Sie konservative Schwellen werte (z. B. min % ausgedrückt, Effekt größe) und ziehen Sie Kombination methoden in Betracht, um vor dem Hochladen robuste Markers ätze abzuleiten.
Gen-Symbole.Stellen Sie eine genaue spezies spezifische Benennung sicher. Fehl paarungen reduzieren die Überlappung zahlen stillschweigend.
Arten/Gewebe stimmen überein.Wählen Sie den nächst gelegenen verfügbaren Gewebe kontext in der Referenz aus, um falsche Übereinstimmungen zu vermeiden.
Interpretation ahr Grund wahrheit.Die Ausgabe hebt signifikante Überschneidungen hervor; bestätigen Sie mit orthogonalen Beweisen (in situ, bekannte Entwicklungs bahnen, Motiv anreicherung usw.).
Omics Empower unterstützt End-to-End-AnlagenEinzel zell sequenz ierungProjekte-insbesondere dort, wo Zell wände und RNasen Dissoziation und RNA-Integrität schwierig machen.
Wir unterstützen akademische Labore, Biotech-Unternehmen und Forschungs kranken häuser bei der zuverlässigen Projekt durchführung in vollem Umfang-von der Proben vorbereitung bis zur Bioinformatik-Analyse.
Mit Labors in Asien, Europa und Nordamerika bieten wir lokalisierte Projekt abwicklung, schnellere Durchlauf zeiten und reaktions schnelle Kommunikation in jeder RegionGe.
Referenz
Chau, T.N., Timilsena, P.R., Bathala, S.P. et al. Ortho loge Marker gruppen zeigen eine breite Zell identitäts konservierung über pflanzliche Einzelzell-Transkript ome. Nat Commun 16, 201 (2025). https://doi.org/10.1038/s41467-024-55755-0
Ja-die ver öffentlichte Methode und das öffentliche Browser zielPflanzenUnd Referenz pflanzen atlanten.
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong
Singapur Globaler Hauptsitz:112 ROBINSON ROAD #03-01
Germany: Arnold-Graffi-Haus / D85 Robert-Rössle-Straße 10 13125 Berlin
Vereinigte Staaten:2 Goddard, Irvine, CA 92618, Vereinigte Staaten
Hong Kong:Wohnung 1019B, 10/F, Liven House, Nr. 61-63 King Yip Street, Kwun Tong